一种由一碳化合物合成苏糖醇的方法及其应用
文献发布时间:2024-04-18 19:58:53
技术领域
本发明属于生物技术领域,具体涉及一种由一碳化合物合成苏糖醇的方法及其应用。
背景技术
苏糖醇是一种四碳糖醇,具有广泛的生物技术应用,包括绿色化学、制药、食品和医药等方面,它是制造很多手性助剂的前体物质,如曲奥舒凡,是一种用于治疗卵巢癌患者的双功能烷基化剂。它还被用来合成间丁酸酯,抗癌药物苏糖醇神经酰胺,白细胞介素-4和干扰素-γ。从苏糖醇还可以衍生合成一系列各种人造的两亲性磷酸盐和合成磷脂,也是响应氧气的颜料的重要组成部分,这种颜料可用于智能的食物包装材料。
目前,苏糖醇主要是通过微生物发酵生产,目前研究最多的方法是以赤藓糖为中间体,通过木糖醇脱氢酶(XDH)合成d-苏糖醇。研究者纯化了一个XDH,研究结果表明,其在体外具有将赤藓酮糖转化为赤藓糖醇和苏糖醇的潜能。后续,通过在解脂耶氏酵母赤藓糖醇生产途径中过表达Ss-XDH,获得了112g/L的d-苏糖醇。但是该微生物发酵方法会产生甘露醇,赤藓糖醇等副产物。同时该微生物发酵法还存在菌体的生长环境控制严苛,后续发酵产物分离纯化困难等问题。
近年来,一碳化合物作为很有应用前景的绿色能源物质得到广泛关注,一碳化合物可以用来合成基本的有机化工原料、燃料和其他高附加值化学品。因其廉价易得的特性,一碳化合物成为替代石油制备高价值化合物最有发展前景的化合物,在医药、食品、化工领域具有重要的科学意义和开发价值。同时一碳化合物的利用和转化也可以显著减少人们在化石燃料利用和合成材料使用过程中对生态环境造成的负面影响。甲醛可以由其他一碳化合物转化而来,进而转化为生物利用的中间物质,同时又兼具来源广泛、价格低廉等特点,以甲醛为前体合成高价值的化合物具有重要的应用前景。
发明内容
本发明的目的是提供一种由甲醛合成苏糖醇的方法及其应用。
为了实现上述目的,本发明首先提供了一种苏糖醇的制备方法。
本发明提供的苏糖醇的制备方法包括如下步骤:以甲醛和甘油为底物在甲醛转化蛋白、D-果糖-6-磷酸醛缩酶、苏糖醇脱氢酶和甘油脱氢酶的作用下反应生成苏糖醇。
上述方法中,所述甲醛转化蛋白可为具有催化甲醛生成羟基乙醛和1,3-二羟基丙酮功能的任意蛋白,包括但不限于本发明中的氨基酸序列如SEQ ID No.3所示的甲醛突变蛋白。
所述D-果糖-6-磷酸醛缩酶可为具有催化甲醛和1,3-二羟基丙酮聚合反应生成赤藓酮糖功能的任意蛋白,包括但不限于本发明中的氨基酸序列如SEQ ID No.4所示的D-果糖-6-磷酸醛缩酶突变蛋白。
所述苏糖醇脱氢酶可为在NADH存在的条件下,具有催化赤藓酮糖生成苏糖醇功能的任意蛋白,包括但不限于本发明中的氨基酸序列如SEQ ID No.1所示的苏糖醇脱氢酶PHM和氨基酸序列如SEQ ID No.2所示的苏糖醇脱氢酶HCS。
所述甘油脱氢酶可为在NAD
进一步的,上述方法的反应体系由甲醛、甘油、NADH、甲醛转化蛋白、D-果糖-6-磷酸醛缩酶、苏糖醇脱氢酶、甘油脱氢酶和缓冲液组成。
所述甲醛在所述反应体系中的初始浓度可为0-2M(不含0M)或0-0.6M(不含0M)或0.6-2M,具体可为0.6M(600mM)或2M。
所述甘油在所述反应体系中的初始浓度可为0-2M(不含0M)或0-0.4M(不含0M)或0.4-2M,具体可为0.4M(400mM)或2M。
所述NADH在所述反应体系中的初始浓度可为0-10mM(不含0mM)或0-2mM(不含0mM)或2-10mM,具体可为2mM或10mM。
所述甲醛转化蛋白在所述反应体系中的初始浓度可为0-20mg/mL(不含0mg/mL)或0-5mg/mL(不含0mg/mL)或5-20mg/mL,具体可为5mg/mL或20mg/mL。
所述D-果糖-6-磷酸醛缩酶在所述反应体系中的初始浓度可为0-20mg/mL(不含0mg/mL)或0-5mg/mL(不含0mg/mL)或5-20mg/mL,具体可为5mg/mL或20mg/mL。
所述苏糖醇脱氢酶在所述反应体系中的初始浓度可为0-20mg/mL(不含0mg/mL)或0-3mg/mL(不含0mg/mL)或3-20mg/mL,具体可为3mg/mL或20mg/mL。
所述甘油脱氢酶在所述反应体系中的初始浓度可为0-20mg/mL(不含0mg/mL)或0-6mg/mL(不含0mg/mL)或6-20mg/mL,具体可为6mg/mL或20mg/mL。
所述缓冲液的pH可为4-9。在本发明的具体实施例中,所述缓冲液为pH为7.4的磷酸钾缓冲液(50mM K
更进一步的,所述反应的条件可为4-50℃、0-1200rpm(不含0rpm)条件下反应0-96h。在本发明的具体实施例中,所述反应的条件可为30℃、1000rpm条件下反应17h。
上述方法中,所述甲醛转化蛋白催化所述甲醛合成二羟丙酮(DHA),进一步被所述D-果糖-6-磷酸醛缩酶催化和所述甲醛反应生成L-赤藓酮糖,所述苏糖醇脱氢酶PHM催化所述L-赤藓酮糖还原生成苏糖醇,所述甘油脱氢酶催化所述甘油还原生成二羟丙酮(DHA),提供辅酶NADH,同时生成的二羟丙酮(DHA)又可以被进一步利用生成苏糖醇。
按照上述方法制备得到的苏糖醇也属于本发明的保护范围。
为了实现上述目的,本发明还提供了一种成套蛋白或与所述成套蛋白相关的生物材料。
本发明提供的成套蛋白由甲醛转化蛋白、D-果糖-6-磷酸醛缩酶、苏糖醇脱氢酶和甘油脱氢酶组成。
本发明提供的与所述成套蛋白相关的生物材料由与甲醛转化蛋白相关的生物材料、与D-果糖-6-磷酸醛缩酶相关的生物材料、与苏糖醇脱氢酶相关的生物材料和与甘油脱氢酶相关的生物材料组成;
所述与甲醛转化蛋白相关的生物材料为编码所述甲醛转化蛋白的核酸分子或含有所述核酸分子的表达盒、重组载体、重组微生物;
所述与D-果糖-6-磷酸醛缩酶相关的生物材料为编码所述D-果糖-6-磷酸醛缩酶的核酸分子或含有所述核酸分子的表达盒、重组载体、重组微生物;
所述与苏糖醇脱氢酶相关的生物材料为编码所述苏糖醇脱氢酶的核酸分子或含有所述核酸分子的表达盒、重组载体、重组微生物;
所述与甘油脱氢酶相关的生物材料为编码所述甘油脱氢酶的核酸分子或含有所述核酸分子的表达盒、重组载体、重组微生物。
上述生物材料中,所述表达盒是指能够在宿主菌或宿主细胞中表达上述甲醛转化蛋白或上述D-果糖-6-磷酸醛缩酶或上述苏糖醇脱氢酶或上述甘油脱氢酶的DNA,该DNA不但可包括启动目的基因转录的启动子,还可包括终止目的基因转录的终止子。进一步,所述表达盒还可包括增强子序列。
所述载体可为质粒、黏粒、噬菌体或病毒载体。所述重组载体可为含有编码上述甲醛转化蛋白或上述D-果糖-6-磷酸醛缩酶或上述苏糖醇脱氢酶或上述甘油脱氢酶的核酸分子的表达载体。
所述重组微生物可为含有上述核酸分子或上述表达盒或上述重组载体的真菌或细菌。所述细菌可为大肠杆菌,具体可为携带DE3基因型的大肠杆菌。
进一步的,编码所述甲醛转化蛋白的核酸分子为如下(a1)或(a2)中任一种:
(a1)SEQ ID No.8所示的DNA分子;
(a2)与(a1)限定的DNA序列具有75%以上同一性且编码所述甲醛突变蛋白的DNA分子。
编码所述D-果糖-6-磷酸醛缩酶的核酸分子为如下(b1)或(b2)中任一种:
(b1)SEQ ID No.9所示的DNA分子;
(b2)与(b1)限定的DNA序列具有75%以上同一性且编码所述D-果糖-6-磷酸醛缩酶突变蛋白的DNA分子。
编码所述苏糖醇脱氢酶的核酸分子为如下(c1)或(c2)中任一种:
(c1)SEQ ID No.6或SEQ ID No.7所示的DNA分子;
(c2)与(c1)限定的DNA序列具有75%以上同一性且编码所述苏糖醇脱氢酶PHM或所述苏糖醇脱氢酶HCS的DNA分子。
编码所述甘油脱氢酶的核酸分子为如下(d1)或(d2)中任一种:
(d1)SEQ ID No.10所示的DNA分子;
(d2)与(d1)限定的DNA序列具有75%以上同一性且编码所述甘油脱氢酶的DNA分子。
上述75%以上同一性可为至少80%、85%、90%、91%、92%、93%、94%、95%、96%、98%、99%或100%的同一性。
更进一步的,所述重组载体可为在载体pET28a的NdeⅠ和XhoⅠ位点间插入SEQ IDNo.6或SEQ ID No.7或SEQ ID No.8或SEQ ID No.9所示DNA片段后得到的重组载体或在载体pET21b的BamHⅠ和NotI位点间插入SEQ ID No.10所示DNA片段后得到的重组载体。所述重组微生物为含有上述重组载体的大肠杆菌BL21 GOLD(DE3)。
为了实现上述目的,本发明最后提供了如下1)-3)任一种应用:
1)上述苏糖醇脱氢酶PHM或上述苏糖醇脱氢酶HCS在催化赤藓酮糖生成苏糖醇中的应用;
2)上述成套蛋白或与所述成套蛋白相关的生物材料在由甲醛生成苏糖醇中的应用;
3)上述成套蛋白或与所述成套蛋白相关的生物材料在制备苏糖醇中的应用。
本发明提供了一种由甲醛合成苏糖醇的方法。本发明以甲醛和甘油为底物,用甲醛转化蛋白催化甲醛合成DHA,进一步被D-果糖-6-磷酸醛缩酶催化和甲醛反应生成L-赤藓酮糖,苏糖醇脱氢酶PHM催化L-赤藓酮糖还原生成苏糖醇,甘油脱氢酶催化甘油还原生成DHA,提供辅酶NADH,同时生成的DHA又可以被进一步利用生成苏糖醇。本发明提供了一条新的甲醛合成苏糖醇的途径,在一锅体系中即可实现甲醛到苏糖醇的转化,具有较好的应用前景。
附图说明
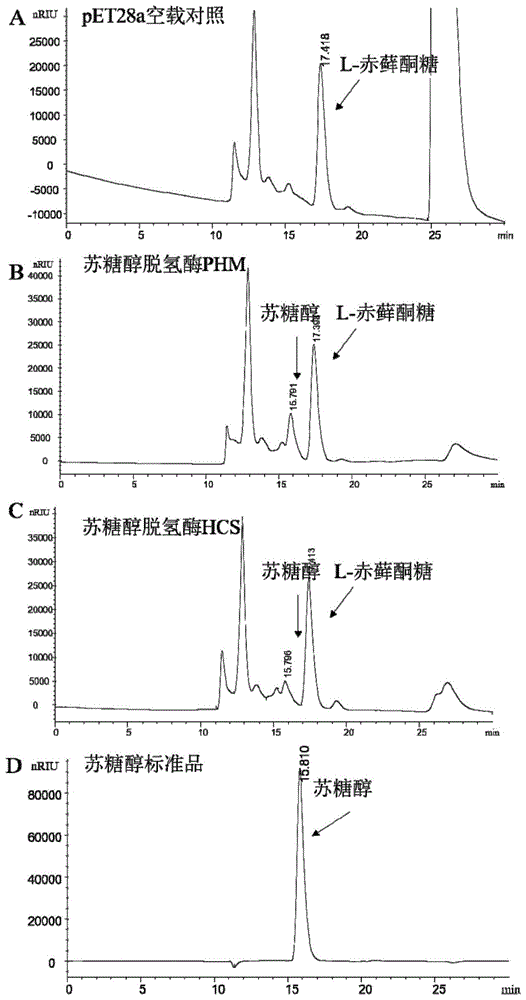
图1为实施例2中HPLC检测苏糖醇脱氢酶PHM和HCS催化L-赤藓酮糖生成苏糖醇。
图2为实施例4中苏糖醇脱氢酶PHM的最适pH。
图3为实施例4中苏糖醇脱氢酶PHM的最适反应温度。
图4为实施例6中从L-赤藓酮糖经酶催化产生苏糖醇。
图5为实施例7中从DHA经酶催化产生苏糖醇。
具体实施方式
下面结合具体实施方式对本发明进行进一步的详细描述,给出的实施例仅为了阐明本发明,而不是为了限制本发明的范围。以下提供的实施例可作为本技术领域普通技术人员进行进一步改进的指南,并不以任何方式构成对本发明的限制。
下述实施例中的实验方法,如无特殊说明,均为常规方法,按照本领域内的文献所描述的技术或条件或者按照产品说明书进行。下述实施例中所用的材料、试剂等,如无特殊说明,均可从商业途径得到。
实施例1、苏糖醇脱氢酶的诱导表达
本发明中的苏糖醇脱氢酶PHM的氨基酸序列如SEQ ID No.1所示,其编码基因序列如SEQ ID No.6所示。
本发明中的苏糖醇脱氢酶HCS的氨基酸序列如SEQ ID No.2所示,其编码基因序列如SEQ ID No.7所示。
上述苏糖醇脱氢酶的诱导表达方法具体如下:将苏糖醇脱氢酶的编码基因序列(SEQ ID No.6或SEQ ID No.7)连接至载体pET28a的NdeⅠ和XhoⅠ位点间,得到重组载体,然后将经测序验证正确的重组载体转入大肠杆菌BL21 GOLD(DE3)中,划线,长出单克隆。挑取单克隆接种于5mL LB培养基中,37℃过夜培养,然后以1%(V/V)接种量接种于100mL LB培养基中,在37℃、200r/min条件下培养。当培养至OD
实施例2、苏糖醇脱氢酶的活性测定
将实施例1中诱导表达完成的各个苏糖醇脱氢酶菌体统一OD
HPLC检测条件:色谱柱:DEVOTE Sugar 10H柱子;流动相:5mM H
结果如图1所示,结果表明:本发明中的苏糖醇脱氢酶PHM和苏糖醇脱氢酶HCS均具有催化L-赤藓酮糖脱氢产生苏糖醇的功能。
实施例3、苏糖醇脱氢酶PHM的纯化
取实施例1中诱导表达完成的苏糖醇脱氢酶PHM菌体,先使用25mL 20mM咪唑缓冲液重悬,高压均质仪破碎菌体,离心收集上清液过0.22μm滤膜。然后利用Ni
实施例4、苏糖醇脱氢酶PHM的最适pH、最适反应温度和动力学参数的测定
1、最适pH
配置pH分别为3、4、5的柠檬酸-柠檬酸钠缓冲液(50mM柠檬酸和柠檬酸钠,5mMMgSO
在不同pH的缓冲液中配制200μL的反应体系,200μL的反应体系含有50μg/mL苏糖醇脱氢酶PHM和8mM赤藓酮糖,然后加入2mM NADH并立即在室温条件下使用酶标仪在340nm下设置动力学法测定20min,并计算吸光度值下降速率。
结果如图2所示,结果表明:苏糖醇脱氢酶PHM在pH6的条件下具有最大的活性,所以苏糖醇脱氢酶PHM的最适pH为6。
2、最适反应温度
在pH为6的磷酸钾缓冲液(50mM K
结果如图3所示,结果表明:苏糖醇脱氢酶PHM在30℃的温度下具有最大的活性,所以苏糖醇脱氢酶PHM的最适反应温度为30℃。
3、动力学参数
在pH为6的磷酸钾缓冲液(50mM K
表1、苏糖醇脱氢酶PHM的动力学参数
实施例5、甲醛突变蛋白、D-果糖-6-磷酸醛缩酶突变蛋白和甘油脱氢酶的诱导表达和纯化
本发明中的甲醛突变蛋白的氨基酸序列如SEQ ID No.3所示,其编码基因序列如SEQ ID No.8所示。
本发明中的D-果糖-6-磷酸醛缩酶突变蛋白的氨基酸序列如SEQ ID No.4所示,其编码基因序列如SEQ ID No.9所示。
本发明中的甘油脱氢酶的氨基酸序列如SEQ ID No.5所示,其编码基因序列如SEQID No.10所示。
上述蛋白的诱导表达与纯化方法具体如下:将甲醛突变蛋白编码基因序列连接至载体pET28a的NdeⅠ和XhoⅠ位点间,得到重组载体1,将D-果糖-6-磷酸醛缩酶突变蛋白编码基因序列连接至载体pET28a的NdeⅠ和XhoⅠ位点间,得到重组载体2,将甘油脱氢酶编码基因序列连接至载体pET21b的BamHⅠ和Not I位点间,得到重组载体3。分别将经测序验证正确的重组载体1-3转入大肠杆菌BL21 GOLD(DE3)中,划线,长出单克隆。挑取单克隆接种于20mLLB培养基中,37℃过夜培养,然后以1%(V/V)接种量接种于600mL LB培养基中,在37℃、200r/min条件下培养。当培养至OD
实施例6、苏糖醇脱氢酶PHM和甘油脱氢酶辅酶循环催化L-赤藓酮糖到苏糖醇
将纯化后的苏糖醇脱氢酶PHM和甘油脱氢酶使用BCA蛋白定量试剂盒进行蛋白定量,在pH 7.4的磷酸钾缓冲液(50mM K
反应体系1(500μL):100mM L-赤藓酮糖,200mM甘油,3mg/mL苏糖醇脱氢酶PHM,6mg/mL甘油脱氢酶,2mM NADH。
反应体系2(500μL):100mM L-赤藓酮糖,200mM甘油,3mg/mL苏糖醇脱氢酶PHM,9mg/mL甘油脱氢酶,2mM NADH。
反应体系3(500μL):100mM L-赤藓酮糖,200mM甘油,3mg/mL苏糖醇脱氢酶PHM,12mg/mL甘油脱氢酶,2mM NADH。
分别将反应体系1-3在30℃、1000rpm条件下反应14h。反应完成后,用3KDa的超滤管去除体系中的酶,进行HPLC检测。
HPLC检测条件:色谱柱:DEVOTE Sugar 10H柱子;流动相:5mM H
结果如图4所示,结果显示:在甘油脱氢酶催化甘油产生二羟丙酮(DHA)的情况下,能够给L苏糖醇脱氢酶PHM产生反应所需要的NADH,达到辅酶循环的效果。苏糖醇的产量能达到40mM左右,同时,进一步增加甘油脱氢酶在反应体系中的浓度比例,对苏糖醇的产量没有明显的增加的作用,所以后续的反应,按照苏糖醇脱氢酶PHM和甘油脱氢酶的质量浓度比为1:2进行。
实施例7、D-果糖-6-磷酸醛缩酶突变蛋白、苏糖醇脱氢酶PHM和甘油脱氢酶催化DHA到苏糖醇
将纯化后的D-果糖-6-磷酸醛缩酶突变蛋白、苏糖醇脱氢酶PHM和甘油脱氢酶使用BCA蛋白定量试剂盒进行蛋白定量,在pH为7.4的磷酸钾缓冲液(50mM K
反应体系1(200μL):100mM DHA,200mM甲醛,200mM甘油,5mg/mL D-果糖-6-磷酸醛缩酶突变蛋白,2mM NADH,3mg/mL苏糖醇脱氢酶PHM,6mg/mL甘油脱氢酶。
反应体系2(200μL):100mM DHA,200mM甲醛,200mM甘油,5mg/mL D-果糖-6-磷酸醛缩酶突变蛋白,2mM NADH,4mg/mL苏糖醇脱氢酶PHM,8mg/mL甘油脱氢酶。
反应体系3(200μL):100mM DHA,200mM甲醛,200mM甘油,5mg/mL D-果糖-6-磷酸醛缩酶突变蛋白,2mM NADH,5mg/mL苏糖醇脱氢酶PHM,10mg/mL甘油脱氢酶。
分别将反应体系1-3在30℃、1000rpm条件下反应14h。反应完成后,用3KDa的超滤管去除体系中的酶,进行HPLC检测。
HPLC检测条件:色谱柱:DEVOTE Sugar 10H柱子;流动相:5mM H
结果如图5所示,结果显示:D-果糖-6-磷酸醛缩酶突变蛋白能够催化DHA和甲醛缩合生成L-赤藓酮糖,L-赤藓酮糖被苏糖醇脱氢酶PHM催化脱氢产生苏糖醇,甘油脱氢酶催化甘油还原生成DHA,提供辅酶NADH,同时生成的DHA又可以进一步和甲醛反应生成L-赤藓酮糖,被还原生成苏糖醇。苏糖醇的产量约为120mM,高于体系中加入的DHA的量,能够得出甘油生成的DHA也被进一步的利用生成苏糖醇。同时,进一步增加苏糖醇脱氢酶PHM在反应体系中的浓度,对苏糖醇的产量没有促进作用,所以后续的反应,按照苏糖醇脱氢酶PHM的量为3mg/mL进行。
实施例8、甲醛突变蛋白、D-果糖-6-磷酸醛缩酶突变蛋白、苏糖醇脱氢酶PHM和甘油脱氢酶催化甲醛经过两步反应生成苏糖醇
将纯化后的甲醛突变蛋白、D-果糖-6-磷酸醛缩酶突变蛋白、苏糖醇脱氢酶PHM和甘油脱氢酶使用BCA蛋白定量试剂盒进行蛋白定量,在pH为7.4的磷酸钾缓冲液(50mMK
HPLC检测条件:色谱柱:DEVOTE Sugar 10H柱子;流动相:5mM H
结果如表2所示,结果显示:第一步反应,甲醛突变蛋白首先催化甲醛生成DHA,第二步反应,D-果糖-6-磷酸醛缩酶突变蛋白催化DHA和甲醛缩合生成L-赤藓酮糖,L-赤藓酮糖被苏糖醇脱氢酶PHM催化脱氢产生苏糖醇,甘油脱氢酶催化甘油还原生成DHA,提供辅酶NADH,同时生成的DHA又可以进一步和甲醛反应生成L-赤藓酮糖,被还原生成苏糖醇。苏糖醇的产量为195.52mM,同时,反应体系中还有88.69mM L-赤藓酮糖剩余。
表2、从甲醛经过两步法酶催化生成苏糖醇
实施例9、甲醛突变蛋白、D-果糖-6-磷酸醛缩酶突变蛋白、苏糖醇脱氢酶PHM和甘油脱氢酶催化甲醛一锅反应生成苏糖醇
将纯化后的甲醛突变蛋白、D-果糖-6-磷酸醛缩酶突变蛋白、苏糖醇脱氢酶PHM和甘油脱氢酶使用BCA蛋白定量试剂盒进行蛋白定量,在pH为7.4的磷酸钾缓冲液(50mMK
HPLC检测条件:色谱柱:DEVOTE Sugar 10H柱子;流动相:5mM H2SO4溶液;紫外检测(210nm)和示差检测;流速:0.5mL/min;柱温:20℃;进样量:20μL。
结果如表3所示,结果显示:在一锅体系中,甲醛经过级联反应被催化生成苏糖醇。苏糖醇的产量为217.52mM,同时,反应体系中还有74.27mM L-赤藓酮糖和21.01mM DHA剩余。
表3、从甲醛经过一锅法酶催化生成苏糖醇
以上对本发明进行了详述。对于本领域技术人员来说,在不脱离本发明的宗旨和范围,以及无需进行不必要的实验情况下,可在等同参数、浓度和条件下,在较宽范围内实施本发明。虽然本发明给出了特殊的实施例,应该理解为,可以对本发明作进一步的改进。总之,按本发明的原理,本申请欲包括任何变更、用途或对本发明的改进,包括脱离了本申请中已公开范围,而用本领域已知的常规技术进行的改变。按以下附带的权利要求的范围,可以进行一些基本特征的应用。
序列表
<110> 中国科学院天津工业生物技术研究所
<120> 一种由一碳化合物合成苏糖醇的方法及其应用
<160> 10
<170> PatentIn version 3.5
<210> 1
<211> 266
<212> PRT
<213> Artificial Sequence
<400> 1
Met Thr Ala Lys Ala Thr Tyr Gln Phe Ala Asp Lys Thr Ile Leu Ile
1 5 1015
Thr Gly Gly Ala Gly Asp Ile Gly Lys Ala Thr Ala His Arg Phe Ala
202530
Ala Asn Gly Ala Gly Ile Ala Leu Leu Asp Leu Asn Glu Pro Lys Met
354045
Ala Asp Val Ala Val Glu Leu Lys Gly Tyr Asn Val Pro Val Gly Thr
505560
Phe Arg Cys Asp Val Thr Ser Ser Asp Asp Val Ala Lys Ala Phe Thr
65707580
Gly Ala Val Lys Gln Leu Gly Arg Ile Asp Tyr Val Phe Asn Asn Ala
859095
Gly Tyr Gln Gly Val Phe Ala Lys Thr Asp Glu Tyr Pro Glu Asp Asp
100 105 110
Phe Gln Lys Val Ile Asn Ile Asn Val Val Gly Val Phe His Ile Leu
115 120 125
Lys Ala Ala Ala Gln Gln Leu Arg Asp Ala Gly Gly Gly Ala Ile Val
130 135 140
Asn Met Ala Ser Tyr Ala Gly Val Val Gly Pro Pro Asn Met Leu Ala
145 150 155 160
Tyr Ala Ala Ser Lys Phe Ala Val Ile Gly Ile Thr Gln Thr Ala Ala
165 170 175
Lys Asp Leu Ala Pro Tyr Gly Ile Arg Val Asn Ala Leu Ser Pro Ala
180 185 190
Leu Ile Gly Pro Gly Phe Met Trp Thr Arg Gln Thr Glu Leu Gln Ala
195 200 205
Ala Val Gly Ser Gln Tyr Phe Asp Ala Asp Pro Lys Val Val Glu Gln
210 215 220
Gln Met Ile Asp Ser Val Pro Met Arg Arg Leu Gly Ser Leu Glu Glu
225 230 235 240
Val Ala Asn Gly Val Ala Phe Leu Met Ser Glu Glu Ala Ser Tyr Ile
245 250 255
Thr Gly Phe Asn Leu Glu Val Thr Gly Gly
260 265
<210> 2
<211> 262
<212> PRT
<213> Artificial Sequence
<400> 2
Met Glu Thr Lys Arg Phe Ser Gly Lys Ser Ile Val Ile Thr Gly Gly
1 5 1015
Ala Gly Asp Ile Gly Leu Ala Thr Ala Val Arg Phe Gly Asn Glu Gly
202530
Ala Asp Val Ala Leu Val Asp Val Lys Asp Met Ala Ser Ala Lys Ala
354045
Lys Val Gln Gln Thr Gly Ala Thr Val Arg Thr Tyr Thr Cys Asp Val
505560
Thr Asp Tyr Ala Gln Val Lys Gln Thr Val Ala Thr Ile Ala Glu Asp
65707580
Phe Gly Ser Ile Asp Met Leu Phe Asn Asn Ala Gly Val Gln Gly Gln
859095
Phe Lys Gln Leu His Thr Tyr Pro Val Asp Asp Phe Ala Gln Val Ile
100 105 110
Asn Ile Asn Leu Ile Gly Ala Phe His Val Leu Arg Ala Val Ala Ile
115 120 125
His Met Val Ala Gln Lys Ser Gly Thr Ile Val Asn Thr Ala Ser Met
130 135 140
Ala Gly Val Asp Gly Pro Val Asn Met Val Ala Tyr Gly Ala Ser Lys
145 150 155 160
Phe Ala Met Val Gly Met Thr Gln Thr Ala Ala Lys Asp Leu Ala Pro
165 170 175
Tyr Gly Ile Arg Val Asn Ser Ile Ser Pro Gly Phe Met Gly Pro Gly
180 185 190
Phe Met Trp Asp Arg Gln Val Asp Leu Gln Ala Ala Val Gly Ser Gln
195 200 205
Tyr Tyr Asp Thr Asp Arg Asn Val Val Ala Lys Gln Met Ile Gly Ala
210 215 220
Val Pro Leu Arg Arg Tyr Gly Asn Ile Glu Glu Ile Pro Gly Thr Val
225 230 235 240
Ala Tyr Leu Met Ser Gly Asp Ser Ser Tyr Val Thr Gly Val Asn Ile
245 250 255
Lys Leu Ser Gly Gly Ile
260
<210> 3
<211> 528
<212> PRT
<213> Artificial Sequence
<400> 3
Met Ala Ser Val His Gly Thr Thr Tyr Glu Leu Leu Arg Arg Gln Gly
1 5 1015
Ile Asp Thr Val Phe Gly Asn Pro Gly Phe Asn Glu Leu Pro Phe Leu
202530
Lys Asp Phe Pro Glu Asp Phe Arg Tyr Ile Leu Ala Leu Gln Glu Ala
354045
Cys Val Val Gly Ile Ala Asp Gly Tyr Ala Gln Ala Ser Arg Lys Pro
505560
Ala Phe Ile Asn Leu His Ser Ala Ala Gly Thr Gly Asn Ala Met Gly
65707580
Ala Leu Ser Asn Ala Arg Thr Ser His Ser Pro Leu Ile Val Thr Ala
859095
Gly Gln Gln Thr Arg Ala Met Ile Gly Val Glu Ala Ser Glu Thr Asn
100 105 110
Val Asp Ala Ala Asn Leu Pro Arg Pro Leu Val Lys Trp Ser Tyr Glu
115 120 125
Pro Ala Ser Ala Ala Glu Val Pro His Ala Met Ser Arg Ala Ile His
130 135 140
Met Ala Ser Met Ala Pro Gln Gly Pro Val Tyr Leu Ser Val Pro Tyr
145 150 155 160
Asp Asp Trp Asp Lys Asp Ala Asp Pro Gln Ser His His Leu Phe Asp
165 170 175
Arg His Val Ser Ser Ser Val Arg Leu Asn Asp Gln Asp Leu Asp Ile
180 185 190
Leu Val Lys Ala Leu Asn Ser Ala Ser Asn Pro Ala Ile Val Leu Gly
195 200 205
Pro Asp Val Asp Ala Ala Asn Ala Asn Ala Asp Cys Val Met Leu Ala
210 215 220
Glu Arg Leu Lys Ala Pro Val Trp Val Ala Pro Ser Ala Pro Arg Cys
225 230 235 240
Pro Phe Pro Thr Arg His Pro Cys Phe Arg Gly Leu Met Pro Ala Gly
245 250 255
Ile Ala Ala Ile Ser Gln Leu Leu Glu Gly His Asp Val Val Leu Val
260 265 270
Ile Gly Ala Pro Val Phe Arg Tyr Tyr Gln Tyr Asp Pro Gly Gln Tyr
275 280 285
Leu Lys Pro Gly Thr Arg Leu Ile Ser Val Thr Cys Asp Pro Leu Glu
290 295 300
Ala Ala Arg Ala Pro Met Gly Asp Ala Ile Val Ala Asp Ile Gly Ala
305 310 315 320
Met Ala Ser Ala Leu Ala Asn Leu Val Glu Glu Ser Ser Arg Gln Leu
325 330 335
Pro Thr Ala Ala Pro Glu Pro Ala Lys Val Asp Gln Asp Ala Gly Arg
340 345 350
Leu His Pro Glu Thr Val Phe Asp Thr Leu Asn Asp Met Ala Pro Glu
355 360 365
Asn Ala Ile Tyr Leu Asn Glu Ser Thr Ser Thr Thr Ala Gln Met Trp
370 375 380
Gln Arg Leu Asn Met Arg Asn Pro Gly Ser Tyr Tyr Phe Cys Ala Ala
385 390 395 400
Gly Gly Leu Gly Phe Ala Leu Pro Ala Ala Ile Gly Val Gln Leu Ala
405 410 415
Glu Pro Glu Arg Gln Val Ile Ala Val Ile Gly Asp Gly Ser Ala Asn
420 425 430
Tyr Ser Ile Ser Ala Leu Trp Thr Ala Ala Gln Tyr Asn Ile Pro Thr
435 440 445
Ile Phe Val Ile Met Asn Asn Gly Thr Tyr Gly Met Leu Arg Trp Phe
450 455 460
Ala Gly Val Leu Glu Ala Glu Asn Val Pro Gly Leu Asp Val Pro Gly
465 470 475 480
Ile Asp Phe Arg Ala Leu Ala Lys Gly Tyr Gly Val Gln Ala Leu Lys
485 490 495
Ala Asp Asn Leu Glu Gln Leu Lys Gly Ser Leu Gln Glu Ala Leu Ser
500 505 510
Ala Lys Gly Pro Val Leu Ile Glu Val Ser Thr Val Ser Pro Val Lys
515 520 525
<210> 4
<211> 220
<212> PRT
<213> Artificial Sequence
<400> 4
Met Glu Leu Tyr Leu Asp Thr Ser Asp Val Val Ala Val Lys Ala Leu
1 5 1015
Ser Arg Ile Phe Pro Leu Ala Gly Val Thr Thr Asn Pro Ser Ile Ile
202530
Ala Ala Gly Lys Lys Pro Leu Asp Val Val Leu Pro Gln Leu His Glu
354045
Ala Met Gly Gly Gln Gly Arg Leu Phe Ala Gln Val Met Ala Thr Thr
505560
Ala Glu Gly Met Val Asn Asp Ala Leu Lys Leu Arg Ser Ile Ile Ala
65707580
Asp Ile Val Val Lys Val Pro Val Thr Ala Glu Gly Leu Ala Ala Ile
859095
Lys Met Leu Lys Ala Glu Gly Ile Pro Thr Leu Gly Thr Ala Val Tyr
100 105 110
Gly Ala Ala Gln Gly Leu Leu Ser Ala Leu Ala Gly Ala Glu Tyr Val
115 120 125
Ser Pro Tyr Val Asn Arg Ile Asp Ala Gln Gly Gly Ser Gly Ile Gln
130 135 140
Thr Val Thr Asp Leu His Gln Leu Leu Lys Met His Ala Pro Gln Ala
145 150 155 160
Lys Val Leu Ala Ala Ser Phe Lys Thr Pro Arg Gln Ala Leu Asp Cys
165 170 175
Leu Leu Ala Gly Cys Glu Ser Ile Thr Leu Pro Leu Asp Val Ala Gln
180 185 190
Gln Met Ile Ser Tyr Pro Ala Val Asp Ala Ala Val Ala Lys Phe Glu
195 200 205
Gln Asp Trp Gln Gly Ala Phe Gly Arg Thr Ser Ile
210 215 220
<210> 5
<211> 367
<212> PRT
<213> Artificial Sequence
<400> 5
Met Asp Arg Ile Ile Gln Ser Pro Gly Lys Tyr Ile Gln Gly Ala Asp
1 5 1015
Val Ile Asn Arg Leu Gly Glu Tyr Leu Lys Pro Leu Ala Glu Arg Trp
202530
Leu Val Val Gly Asp Lys Phe Val Leu Gly Phe Ala Gln Ser Thr Val
354045
Glu Lys Ser Phe Lys Asp Ala Gly Leu Val Val Glu Ile Ala Pro Phe
505560
Gly Gly Glu Cys Ser Gln Asn Glu Ile Asp Arg Leu Arg Gly Ile Ala
65707580
Glu Thr Ala Gln Cys Gly Ala Ile Leu Gly Ile Gly Gly Gly Lys Thr
859095
Leu Asp Thr Ala Lys Ala Leu Ala His Phe Met Gly Val Pro Val Ala
100 105 110
Ile Ala Pro Thr Ile Ala Ser Thr Asp Ala Pro Cys Ser Ala Leu Ser
115 120 125
Val Ile Tyr Thr Asp Glu Gly Glu Phe Asp Arg Tyr Leu Leu Leu Pro
130 135 140
Asn Asn Pro Asn Met Val Ile Val Asp Thr Lys Ile Val Ala Gly Ala
145 150 155 160
Pro Ala Arg Leu Leu Ala Ala Gly Ile Gly Asp Ala Leu Ala Thr Trp
165 170 175
Phe Glu Ala Arg Ala Cys Ser Arg Ser Gly Ala Thr Thr Met Ala Gly
180 185 190
Gly Lys Cys Thr Gln Ala Ala Leu Ala Leu Ala Glu Leu Cys Tyr Asn
195 200 205
Thr Leu Leu Glu Glu Gly Glu Lys Ala Met Leu Ala Ala Glu Gln His
210 215 220
Val Val Thr Pro Ala Leu Glu Arg Val Ile Glu Ala Asn Thr Tyr Leu
225 230 235 240
Ser Gly Val Gly Phe Glu Ser Gly Gly Leu Ala Ala Ala His Ala Val
245 250 255
His Asn Gly Leu Thr Ala Ile Pro Asp Ala His His Tyr Tyr His Gly
260 265 270
Glu Lys Val Ala Phe Gly Thr Leu Thr Gln Leu Val Leu Glu Asn Ala
275 280 285
Pro Val Glu Glu Ile Glu Thr Val Ala Ala Leu Ser His Ala Val Gly
290 295 300
Leu Pro Ile Thr Leu Ala Gln Leu Asp Ile Lys Glu Asp Val Pro Ala
305 310 315 320
Lys Met Arg Ile Val Ala Glu Ala Ala Cys Ala Glu Gly Glu Thr Ile
325 330 335
His Asn Met Pro Gly Gly Ala Thr Pro Asp Gln Val Tyr Ala Ala Leu
340 345 350
Leu Val Ala Asp Gln Tyr Gly Gln Arg Phe Leu Gln Glu Trp Glu
355 360 365
<210> 6
<211> 801
<212> DNA
<213> Artificial Sequence
<400> 6
atgaccgcta aagctaccta ccagttcgct gacaaaacca tcctgatcac cggtggtgct 60
ggtgacatcg gtaaagctac cgctcaccgt ttcgctgcta acggtgctgg tatcgctctg 120
ctggacctga acgaaccgaa aatggctgac gttgctgttg aactgaaagg ttacaacgtt 180
ccggttggta ccttccgttg cgacgttacc tcttctgacg acgttgctaa agctttcacc 240
ggtgctgtta aacagctggg tcgtatcgac tacgttttca acaacgctgg ttaccagggt 300
gttttcgcta aaaccgacga atacccggaa gacgacttcc agaaagttat caacatcaac 360
gttgttggtg ttttccacat cctgaaagct gctgctcagc agctgcgtga cgctggtggt 420
ggtgctatcg ttaacatggc ttcttacgct ggtgttgttg gtccgccgaa catgctggct 480
tacgctgctt ctaaattcgc tgttatcggt atcacccaga ccgctgctaa agacctggct 540
ccgtacggta tccgtgttaa cgctctgtct ccggctctga tcggtccggg tttcatgtgg 600
acccgtcaga ccgaactgca ggctgctgtt ggttctcagt acttcgacgc tgacccgaaa 660
gttgttgaac agcagatgat cgactctgtt ccgatgcgtc gtctgggttc tctggaagaa 720
gttgctaacg gtgttgcttt cctgatgtct gaagaagctt cttacatcac cggtttcaac 780
ctggaagtta ccggtggtta a 801
<210> 7
<211> 789
<212> DNA
<213> Artificial Sequence
<400> 7
atggaaacca aacgtttctc tggtaaatct atcgttatca ccggtggtgc tggtgacatc 60
ggtctggcta ccgctgttcg tttcggtaac gaaggtgctg acgttgctct ggttgacgtt 120
aaagacatgg cttctgctaa agctaaagtt cagcagaccg gtgctaccgt tcgtacctac 180
acctgcgacg ttaccgacta cgctcaggtt aaacagaccg ttgctaccat cgctgaagac 240
ttcggttcta tcgacatgct gttcaacaac gctggtgttc agggtcagtt caaacagctg 300
cacacctacc cggttgacga cttcgctcag gttatcaaca tcaacctgat cggtgctttc 360
cacgttctgc gtgctgttgc tatccacatg gttgctcaga aatctggtac catcgttaac 420
accgcttcta tggctggtgt tgacggtccg gttaacatgg ttgcttacgg tgcttctaaa 480
ttcgctatgg ttggtatgac ccagaccgct gctaaagacc tggctccgta cggtatccgt 540
gttaactcta tctctccggg tttcatgggt ccgggtttca tgtgggaccg tcaggttgac 600
ctgcaggctg ctgttggttc tcagtactac gacaccgacc gtaacgttgt tgctaaacag 660
atgatcggtg ctgttccgct gcgtcgttac ggtaacatcg aagaaatccc gggtaccgtt 720
gcttacctga tgtctggtga ctcttcttac gttaccggtg ttaacatcaa actgtctggt 780
ggtatctaa 789
<210> 8
<211> 1587
<212> DNA
<213> Artificial Sequence
<400> 8
atggcttctg ttcacggtac cacctacgaa ctgctgcgtc gtcagggtat cgacaccgtt 60
ttcggtaacc cgggttttaa cgaactgccg ttcctaaaag acttcccgga agacttccgt 120
tacatcctgg ctctgcagga agcttgcgtt gttggtatcg ctgacggtta cgctcaggct 180
tctcgtaaac cggctttcat caacctgcac tctgctgctg gtaccggtaa cgctatgggt 240
gctctgtcta acgctcgtac ctctcactct ccgctgatcg ttaccgctgg tcagcagacc 300
cgtgctatga tcggtgttga agctagtgaa accaacgttg acgctgctaa cctgccgcgt 360
ccgctggtta aatggtctta cgaaccggct tctgctgctg aagttccgca cgctatgtct 420
cgtgctatcc acatggcttc tatggctccg cagggtccgg tttacctgtc tgttccgtac 480
gacgactggg acaaagacgc tgacccgcag tctcaccacc tgttcgaccg tcacgtttct 540
tcttctgttc gtctgaacga ccaggacctg gacatcctgg ttaaagctct gaactctgct 600
tctaacccgg ctatcgttct gggtccggac gttgacgctg ctaacgctaa cgctgactgc 660
gttatgctgg ctgaacgtct gaaagctccg gtttgggttg ctccgtctgc tccgcgttgc 720
ccgttcccga cccgtcaccc gtgcttccgt ggtctgatgc cggctggtat cgctgctatc 780
tctcagctgc tggaaggtca cgacgttgtt ctggttatcg gtgctccggt tttccgttac 840
taccagtacg acccgggtca gtacctgaaa ccgggtaccc gtctgatctc tgttacctgc 900
gacccgctgg aagctgctcg tgctccgatg ggtgacgcta tcgttgctga catcggtgct 960
atggcttctg ctctggctaa cctggttgaa gaatcttctc gtcagctgcc gaccgctgct 1020
ccggaaccgg ctaaagttga ccaggacgct ggtcgtctgc acccggaaac cgttttcgac 1080
accctgaacg acatggctcc ggaaaacgct atctacctga acgaatctac ctctaccacc 1140
gctcagatgt ggcagcgtct gaacatgcgt aacccgggtt cttactactt ctgcgctgct 1200
ggtggtctgg gtttcgctct gccggctgct atcggtgttc agctggctga accggaacgt 1260
caggttatcg ctgttatcgg tgacggttct gctaactact ctatctctgc tctgtggacc 1320
gctgctcagt acaacatccc gaccatcttc gttatcatga acaacggtac ctacggtatg 1380
ctgcgttggt tcgctggtgt tctggaagct gaaaacgttc cgggtctgga cgttccgggt 1440
atcgacttcc gtgctctggc taaaggttac ggtgttcagg ctctgaaagc tgacaacctg 1500
gaacagctga aaggttctct gcaggaagct ctgtctgcta aaggtccggt tctgatcgaa 1560
gtttctaccg tttctccggt taaataa 1587
<210> 9
<211> 663
<212> DNA
<213> Artificial Sequence
<400> 9
atggaactgt atctggatac ttcagacgtt gttgcggtga aggcgctgtc acgtattttt 60
ccgctggcgg gtgtgaccac taacccaagc attatcgccg cgggtaaaaa accgctggat 120
gttgtgcttc cgcaacttca tgaagcgatg ggcggtcagg ggcgtctgtt tgcccaggta 180
atggctacca ctgccgaagg gatggttaat gacgcgctta agctgcgttc tattattgcg 240
gatatcgtgg tgaaagttcc ggtgaccgcc gaggggctgg cagctattaa gatgttaaaa 300
gcggaaggga ttccgacgct gggaaccgcg gtatatggcg cagcacaagg gctgctgtcg 360
gcgctggcag gtgcggaata tgtttcgcct tacgttaatc gtattgatgc tcagggcggt 420
agcggcattc agactgtgac cgacttacac cagttattga aaatgcatgc gccgcaggcg 480
aaagtgctgg cagcgagttt caaaaccccg cgtcaggcgc tggactgctt actggcagga 540
tgtgaatcaa ttactctgcc actggatgtg gcacaacaga tgattagcta tccggcggtt 600
gatgccgctg tggcgaagtt tgagcaggac tggcagggag cgtttggcag aacgtcgatt 660
taa 663
<210> 10
<211> 1104
<212> DNA
<213> Artificial Sequence
<400> 10
atggaccgca ttattcaatc accgggtaaa tacatccagg gcgctgatgt gattaatcgt 60
ctgggcgaat acctgaagcc gctggcagaa cgctggttag tggtgggtga caaatttgtt 120
ttaggttttg ctcaatccac tgtcgagaaa agctttaaag atgctggact ggtagtagaa 180
attgcgccgt ttggcggtga atgttcgcaa aatgagatcg accgtctgcg tggcatcgcg 240
gagactgcgc agtgtggcgc aattctcggt atcggtggcg gaaaaaccct cgatactgcc 300
aaagcactgg cacatttcat gggtgttccg gtagcgatcg caccgactat cgcctctacc 360
gatgcaccgt gcagcgcatt gtctgttatc tacaccgatg agggtgagtt tgaccgctat 420
ctgctgttgc caaataaccc gaatatggtc attgtcgaca ccaaaatcgt cgctggcgca 480
cctgcacgtc tgttagcggc gggtatcggc gatgcgctgg caacctggtt tgaagcgcgt 540
gcctgctctc gtagcggcgc gaccaccatg gcgggcggca agtgcaccca ggctgcgctg 600
gcactggctg aactgtgcta caacaccctg ctggaagaag gcgaaaaagc gatgcttgct 660
gccgaacagc atgtagtgac tccggcgctg gagcgcgtga ttgaagcgaa cacctatttg 720
agcggtgttg gttttgaaag tggtggtctg gctgcggcgc acgcagtgca taacggcctg 780
accgctatcc cggacgcgca tcactattat cacggtgaaa aagtggcatt cggtacgctg 840
acgcagctgg ttctggaaaa tgcgccggtg gaggaaatcg aaaccgtagc tgcccttagc 900
catgcggtag gtttgccaat aactctcgct caactggata ttaaagaaga tgtcccggcg 960
aaaatgcgaa ttgtggcaga agcggcatgt gcagaaggtg aaaccattca caacatgcct 1020
ggcggcgcga cgccagatca ggtttacgcc gctctgctgg tagccgacca gtacggtcag 1080
cgtttcctgc aagagtggga ataa 1104
